![]()
La domesticación de Penicillium: lectura del genoma del moho productor de penicilina
Alexander Fleming decía que descubrir la penicilina, hace ahora 80 años, no ocurrió porque el moho que la produce le gritase que sintetizaba este antibiótico. Si el moho pudiera hablar probablemente nos diría que tampoco su objetivo en la vida es producir penicilina, pero para nosotros el Penicillium, además de estropear frutas y pan, sirve exactamente para eso. Esta semana se ha publicado en internet la secuencia de su genoma y la comparación de la actividad de sus genes en dos estirpes, siendo una de ellas productora de penicilina en cantidad mucho mayor de lo normal. Podríamos decir que el trabajo cuenta cómo se ha domesticado a un moho.

Una docena de laboratorios, la mitad de ellos de los Países Bajos y dos de León, han unido sus esfuerzos para averiguar la secuencia del genoma de la estirpe Penicillium chrysogenum Wisconsin54-1255, y para comparar su funcionamiento con el de otraestirpe, DS17690, mejorada para producir más cantidad del antibiótico. Sabemos así que este Penicillium contiene casi 13000 genes funcionales, y unos quinientos que no son operativos. Casi un 30% de los genes son específicos de Penicillium, y lo más interesante es que los genes que intervienen en la producciónde penicilina parecen haber derivado de organismos procariotas, los que como las bacterias y a diferencia de los hongos (y de nuestras células) no tienen su material genético separado del citoplasma. Otra característica de alguno de estos genes es que, al igual que ocurre con los genes de las bacterias, no tienen intrones, los segmentos de ADN que, intercalados dentro de los genes, no contienen información traducible en proteína y que son excluidos por las células eucariotas (las que tienen el ADN en un núcleo separado) a la hora de expresar su información genética.
El proceso de domesticación
Cuandolos investigadores han comparado las dos estirpes en condiciones de producción y no producción de penicilina han encontrado que 2470 de sus genes funcionan a diferente ritmo según el caso. Entre ellos se encuentran bastantes de los genes que se sabe están directamente implicados en la síntesis del antibiótico y de sus precursores. La producción de altos niveles de penicilina no parece depender exclusivamente de la capacidad de sintetizarla, sino también de la eficacia de su transporte desde el citoplasma del moho hacia el exterior, y precisamente se observa que un buen número de los genes que codifican sistemas de transporte funcionan más en las dos estirpes cuando están en las condiciones de producir el antibiótico. Sin embargo, de entre todos los numerosos transportadores que codifica elgenoma, 51 de ellos del tipo del que se supone sirve para transportar la penicilina, no se ha podido todavía identificar cuál de ellos es el que lo hace. Los investigadores sospechan que quizás el transporte de la penicilina puede, como ocurre con muchos procesos biológicos, realizarse por más de una vía.
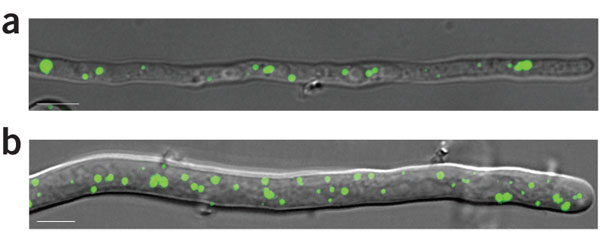
Abundancia de microcuerpos en la estirpe superproductora de penicilina. Los peroxisomas son unas microestructuras en las que suceden las dos últimas etapas de la síntesis de penicilina. En estas dos fotografías de hifas de Pencillium los microcuerpos aparecen con fluorescencia verde producida por una proteína recombinante que contiene una señal que la integra a las membranas del peroxisoma y la proteína fluorescente verde de una medusa. La hifa de la imagen “b” es la que corresponde a la estirpe superproductora, DS17690.
No se puede ir en la procesión y estar repicando las campanas
Parece que la intensificación del funcionamiento de genes dedicados a la síntesis del antibiótico y de su transporte está acompañada por una disminución de la actividad de otros genes cuyos productos dirigen los procesos celulares de mantenimiento de la forma y de la diferenciación, lo que casa con el aspecto diferente de las estirpes que más antibiótico producen. Los investigadores piensan que todavía cabe la posibilidad de aumentar más la eficiencia en la producción de penicilina, por ejemplo inactivando por completo la inducción de la vía que degrada al ácido fenilacético.
A mí me surgen dos reflexiones, por un lado, de los resultados ahora publicados parece que la adaptación a producir mayores cantidades de penicilina se ha conseguido por medio de cambios, duplicaciones y deleciones que se han ido compensando en el genoma a lo largo de las distintas fases de mejora a que se han sometido las estirpes industriales de Penicillium. Queda por ver si los científicos serán capaces de diseñar no solo cambios que sobre el papel supongan una eficacia mayor, sino si podrán anticiparse a la respuesta del moho, al que lógicamente no se le puede forzar a hacer milagros y por lo tanto reducirá la actividad de otros procesos. Para que esto se consiga será necesario progresar mucho más en el conocimiento que se tiene de la fisiología celular, no olvidemos que la genómica nos suministra tan solo el texto y que por ahora somos casi como un niño al que se le diese un ejemplar de Hamlet cuando acaba de aprender a leer, ¿cuánto tardará en comprender lo que evoca el monólogo ante la calavera de Yorik?
Por otra parte, como la misión del Pencillium queda claro que no es darnos penicilina a nosotros, me parece que aprenderíamos mucho estudiando ahora el fenómeno inverso a la selección de cepas superproductoras. Si ponemos a competir a una de ellas con una estirpe silvestre posiblemente no prospere, pero ¿qué cambios le permitirían hacerlo?, ¿cuántos cambios serían precisos?, ¿se recuperaría el genotipo silvestre?, ¿o se conseguirían otras combinaciones? quizás todo esto arrojaría alguna luz sobre las incógnitas que aún tenemos sobre la fisiología de Penicillium.
REFERENCIA
van den Berg et al. Genome sequencing and analysis of the filamentous fungus Penicillium chrysogenum. Nature Biotechnology. ?Published online: 28 September 2008 | doi:10.1038/nbt.1498

Foro del día en madridiario

Hola Miguel,
En relación con la aparición de resistencias a antibióticos nos acaba de surgir una duda. En el penúltimo comentario a esta entrada del blog:
http://weblogs.madrimasd.org/biologia_pensamiento/archive/2008/07/14/96808.aspx
Ángel me pregunta acerca de cómo tiene lugar dicha aparición. Me he atrevido a contestarle, pero seguro que si tienes cinco minutos podrás aclarar dudas que hayan quedado en mi respuesta a su pregunta. Te agradecería una ayudita al respecto. Después de todo la cuestión tiene que ver con esta entrada porque no creo que sea descabellado suponer que, si tanto la síntesis como la resistencia a antibióticos se han podido transmitir en plásmidos, sus genes codificantes se habrán "embarcado" en plásmidos por mecanismos comunes. Enfin, te invito a que leas tanto el comentario de Ángel como el mio contestándole a ver si se te ocurre algo,….
Un abrazo,
Emilio
Hola Emilio,
las resistencias aparecer no "aparecen", se seleccionan, o sea, llega el antibiótico y se carga cuanto bicho hay, menos a lo que es resistente. Si a lo que se refiere la pregunta es a cómo surgieron por vez primera en el universo de los vivos, pues puede aventurarse que debieron hacerlo a la par que la capacidad de producir el antibiótico, de otra forma el productor se hubiera muerto. En un trabajo de hace ya años el grupo de Julian Davies mostraba por técnicas de amplificación de PCR, que muestras de antibióticos comerciales contienen ADN que corresponde a genes de resistencia a cada antibiótico.
El diferente punto de vista que puedo ofrecer es que no existe, por el momento y que yo conozca, pruebas de que haya mutaciones específicas que se induzcan como respuesta asimismo específica a una determinada condición ambiental, ya tuviste una larga discusión con Manuel Sánchez al respecto. Su argumentación, a la que remito al lector, era un buen reflejo de lo que la genética bacteriana ha podido indagar.
http://weblogs.madrimasd.org/microbiologia/archive/2008/06/28/95704.aspx
Lo que ocurre es que el término "adaptativo" parece que lo usamos con significados diferentes. La resistencia a un antibiótico efectivamente "adapta" a la bacteria resistente a vivir en presencia del mismo, pero el antibiótico no es en principio, y salvo lo que enseguida comento, lo que se llamaría un agente mutagénico. Sin embargo sí que se sabe que algún que otro antibiótico dispara mecanismos de defensa que modifican el metabolismo de ADN, lo mismo que puede hacer la luz ultravioleta, y en ese caso los mecanismos de reparación de los daños provocados son más propensos al error, es decir que contribuyen a aumentar la frecuencia de mutación. Asimismo se puede aumentar la frecuencia de salto de secuencias de inserción y transposones, que son asimismo sucesos que pueden aumentar la frecuencia de mutación.
Añadiré que a la vez que la resistencia "adapta" a la bacteria a vivir ignorando el antibiotico, la "desadapta" a vivir sin él (las resistencias tienen lo que se llama un "coste adaptativo", por lo que quitado el antibiótico se tenderán a seleccionar individuos que hayan revertido, perdido o compensado la mutación.
Las bacterias usan quizás una lógica diferente a la humana, no les importa morirse muchas porque por su elevado número siempre acaba quedando alguna y además se dedican a producir cuanta mutación les apetece, mutación que suele acabar con la posibilidad de que su portadora perviva, salvo si vienen mal dadas y resulta que por pura chimba eso le resulta ventajoso sobre las otras. Claro está que hay mutaciones que son letales, y a esas no las salva ni San Lamarck ni San Darwin. Pero les da igual porque como ya digo son muchas y lo ensayan todo.
La anécdota de los peces (vaya el lector al foro correspondiente, con paciencia porque está muy al final de una muy larga discusion http://weblogs.madrimasd.org/biologia_pensamiento/archive/2008/07/14/96808.aspx), que no me atrevo a calificar de experimento, carece, tal como se cuenta, de controles, creo, y me explico. Al menos hubiera sido necesario obtener puestas y desarrollar a los alevines en aguas no contaminadas. Tras varias generaciones volverlos al agua contaminada y si no la palmaban todos contar la frecuencia y compararla con la frecuencia de una población no expuesta nunca. De la comparación de ambas se podría calcular si el paso por el agua contaminada había seleccionado individuos con mutaciones favorables a la supervivencia en los contaminantes. Y si así era habría que estudiar los efectos de los contaminantes sobre el genoma del bicho, porque probablemente se produjese daño cromosómico que se reparase asimismo por sistemas propensos a error como en las bacterias. No se si el experimento está hecho y tampoco yo me conozco el funcionamiento de los vertebrados tan bien como para asegurar lo que uno esperaría que resultase tratándose de peces, que además de eucariotas son ellos muy diploides.
Bueno pues seguro que podéis seguir discutiendo, yo no quiero alargar la respuesta más, ya son las tantas.
Un saludo
Miguel Vicente
Gracias Miguel, por tu aportación tan generosa y erudita.
Ya veo que no hemos adelantado mucho respecto a la anterior discusión y que el origen de la mutación que da lugar a la resistencia sigue en penumbra.
Respecto de los peces, en el sentido que nos interesa al menos, si que había un "cierto" control. Los peces, antes de soltarlos en aguas contaminadas, debían estar pre-adaptados o condicionados, si no lo estaban se morían.
Todo muy interesante. Seguiremos en contacto,
Un saludo,
Emilio
Hola Emilio,
no, no sigue en penumbra, lo que pasa es que es muy complejo, primero porque cada resistencia se debe a un mecanismo diferente, e incluso para un mismo antibiótico hay diversos mecanismos de resitencia. El origen de cada uno de los casos sí que parece pertenecer al mundo de las explicaciones más plausibles, ya que pruebas, pruebas, lo que se dice pruebas de las de hacer un experimento, en paleontología son difíciles.
Hay colegas que opinan que las resistencias las confieren genes que tienen una función específica en el ambiente, te remito a la publicación de José Luis Martínez en Science:
http://www.sciencemag.org/cgi/content/abstract/321/5887/365
y al artículo de Julian Davies en este mismo foro:
http://weblogs.madrimasd.org/microbiologia/archive/2008/09/20/101365.aspx
Hay resistencias que son simples bombas de transporte que funcionan para, además de otros compuestos, expulsar al antibiótico, hay otras que modiifcan al antibiótico y lo inactivan, y otras que directamente lo degradan. Hay otros casos como la resistencia a vancomicina en la que la complejidad de las resistencias es tal que llevaría media hora el explicarlo, pero es muy ilustrativo porque los resistentes la verdad es que llevan una vida perra, pero viven, ver:
http://weblogs.madrimasd.org/microbiologia/archive/2008/02/23/85217.aspx
De todas maneras lo que nos cuenta la genética molecular es que la mutación es previa a la selección y se origina AL AZAR por los errores en la replicación y en el intento de corregirlos, o por saltos de secuencias de inserción (transposones, integrones, etc). Estos fallos e inestabilidad genética son lo normal en la multiplicación rutinaria de las bacterias, incluso cuando más felices son.
Con los peces, el control que me cuentas creo que no es el control, más me parece que es el experimento. El control que yo te decía es contar cuántos descendientes mantienen la capacidad de vivir en el agua contaminada tras reproducirlos varias generaciones realizadas en agua limpia. Eso es herencia, lo otro creo que no. Si se mueren todos se acabó el experimento, no se hereda la adapatación. Y ya decía, si se demostrase que la frecuencia de supervivientes es mayor que la que se encuentra en la población parental nunca expuesta a la contaminación, aún quedaría un largo camino experimental para esclarecer los mecanismos moleculares implicados, que probablemente no tengan nada que ver con la herencia de caracteres adquiridos sino con los mecanismos de reparación de daño genético, un tema de gran interés y enorme repercusión aplicada.
Sinceramente no creo que los postulados de Lamarck se puedan mantener como el mecanismo que ha originado la diversidad de los seres vivos. Tampoco, como ya comenté en otro lugar, la supervivencia de los mejor adaptados puede a mi entender mantenerse tal cual se formuló. Ambas teorías tuvieron su momento y estuvieron muy bien, pero por suerte la Biología ha cambiado y es cada vez, en su detalle, más bonita. ¡Si Darwin, Wallace y Lamarck lo pudieran ver!
http://weblogs.madrimasd.org/microbiologia/archive/2008/06/28/95704.aspx
Incluso nos permite vislumbrar cómo algunos sucesos pudieran haber ocurrido hace millones (y hasta miles de millones) de años:
http://weblogs.madrimasd.org/microbiologia/archive/2008/03/23/87138.aspx
http://weblogs.madrimasd.org/microbiologia/archive/2008/08/17/98871.aspx
Un saludo
Miguel Vicente
Hola Miguel
Una pequeña corrección. Quien encontró el melón en el supermercado de Peoria no fue un ama de casa. Fue la técnico de laboratorio Mary Hunt, también conocida como "Mouldy Mary" porque era la encargada de buscar hiperproductores de penicilina de las diversas muestras que mandaban al laboratorio de Florey. Lo más gracioso fue que encontró el hiperproductor a la vuelta de la esquina despues de haber procesado sin éxito casi un millar de muestras de todas partes del mundo.
Un saludo
http://curiosidadesdelamicrobiologia.blogspot.com/
[…] producía el hongo que aisló Fleming, se pasó a los más de 7000 de las cepas utilizadas para la producción industrial del antibiótico. Además del progreso científico, el desarrollo industrial en España y la […]