![]()

El (cito)Esqueleto de Loki

Las arqueas asgardianas no son un nuevo grupo de superheroínas de la Marvel. Son un tipo de microorganismos procariotas descubiertos en el año 2015 en unos sedimentos provenientes de la chimenea hidrotermal conocida como «Castillo de Loki» en las profundidades del Océano Ártico. En el mundo de la microbiología y la evolución, las arqueas pertenecientes al superphylum Asgard son famosas porque se piensa que, hace unos 2.000 millones de años, uno de sus antecesores fue el que consiguió establecer una endosimbiosis con una proteobacteria, dando lugar a la primera célula eucariota, de la cual descendemos.

En la anterior entrada del blog Mingo y Miguel nos explicaron la conservación filogenética del agrupamiento dcw, donde se encuentran los genes encargados de que se sintetice la pared bacteriana y del divisoma. Entre esos genes hay unos cuantos que codifican para proteínas con función estructural como FtsZ y FtsA, que son homólogos de las proteínas eucariotas tubulina y actina respectivamente. También hay homólogos en las arqueas y eso indica que el ancestro de todas esas proteínas surgió antes de la separación entre los diferentes dominios. Pero también hay otras proteínas que solo se encuentran en uno de los dominios y no en los otros. Cuando uno se pone a comparar las secuencias de las proteínas presentes en bacterias, arqueas y eucariotas lo que aparece es un árbol filogenético en el que las arqueas siempre están cerca de los eucariotas. De hecho, algunas arqueas tienen cientos de genes que codifican para proteínas que se postuló que eran exclusivas de los eucariotas y que son conocidas como ESPs (por eukaryotic signature proteins).
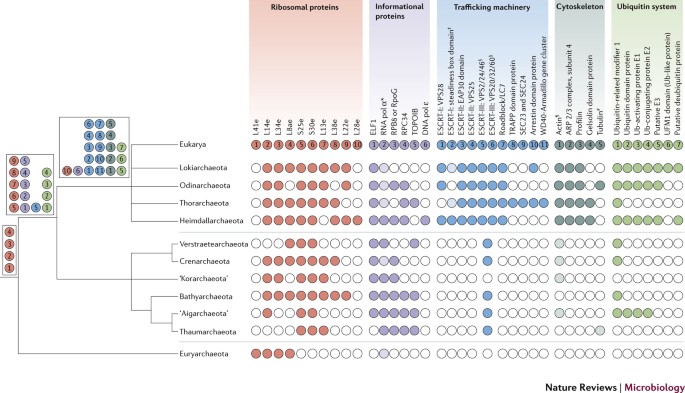
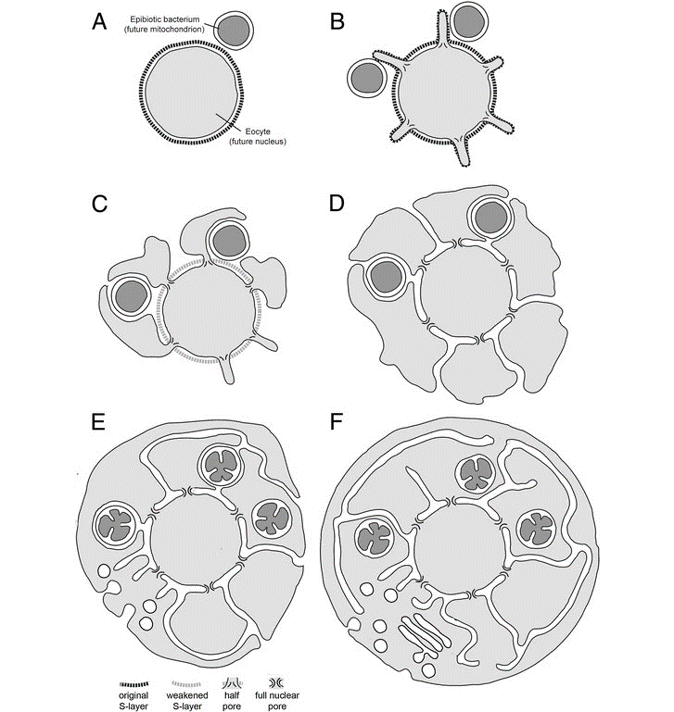
Cuando se descubrieron las arqueas asgardianas se encontró que sus genomas tenían un gran porcentaje de genes ESPs, entre ellos los que codifican para el sistema ESCRT, implicado en la arquitectura de las membranas intracelulares. También se hallaron varios homólogos de actina y de proteínas que se unen a actina muy conservados, lo que podía indicar que esas arqueas poseen un citoesqueleto. Lo malo es que no parecían fáciles de estudiar. En el 2020 se consiguió aislar y crecer a la primera arquea asgardiana. Prometheoarchaeum syntrophicum es un microbio de crecimiento muy lento (hasta 60 días para duplicarse), muy pequeño, y con una morfología celular muy curiosa. Son unos pequeños cocoides que presentan unas delgadas protrusiones en su membrana. Se postuló que esas protrusiones podrían estar presentes en la arquea ancestral que permitió la endosimbiosis mediante un modelo “de dentro hacia fuera”. Es decir, la arquea ancestral proyectó extrusiones que envolvieron a la bacteria simbionte y esas extrusiones se hicieron poco a poco más complicadas formando la envoltura nuclear y el retículo endoplasmático. El otro modelo, mucho más conocido, es el “de fuera hacia dentro”, en el que se postula que la bacteria fue engullida por la arquea y tanto el núcleo como el retículo endoplasmático son el resultado de posteriores invaginaciones de la membrana.
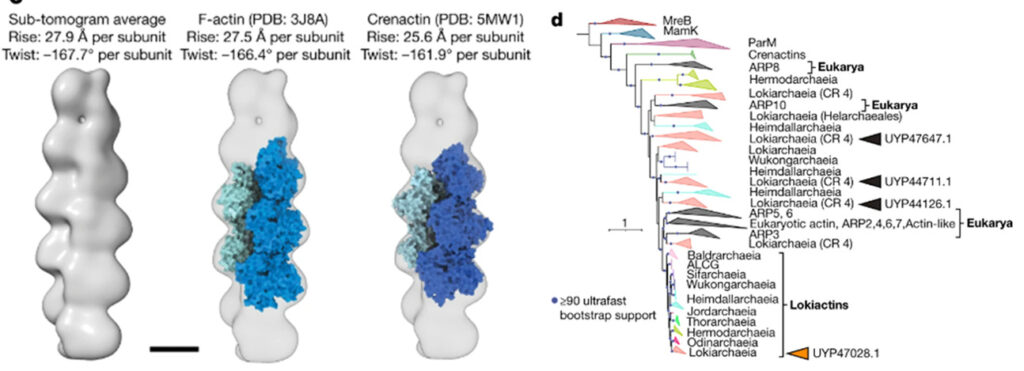
Ahora, el grupo liderado por Martin Pilhofer y Christa Schleper han conseguido crecer a la segunda arquea asgardiana y la han bautizado como Lokiarchaeum ossiferum. Lo mejor de este microbio es que puede crecer heterotróficamente en anaerobiosis a 20ºC, se divide cada 7 a 14 días y los cultivos pueden llegar a alcanzar densidades celulares de 5 × 107 células por mililitro. Al analizar su genoma han encontrado que el 5% de sus genes son ESPs y que entre ellos había 4 homólogos de la actina, y que fueron bautizados como lokiactinas. Su morfología recuerda a la de P. syntrophicum, pero algo más grande y con unas protrusiones muy peculiares, ya que son ramificadas y con constricciones.

Mediante el uso de tomografía crio-electrónica han podido observar su organización intracelular. L. ossiferum presenta una única membrana celular que contiene estructuras bastante complejas. En su interior se observa un citoesqueleto formado por una serie de filamentos en doble hélice que se extiende por las protusiones y las constricciones. Utilizando una inmunotinción han determinado que esos filamentos están compuestos por subunidades de Lokiactina. Los filamentos de este citoesqueleto se disponen cercanos a la periferia celular o en el interior de las protrusiones, de manera bastante similar a cómo se dispone la actina de los ecuariotas.
Quizás lo más interesante del artículo es que han desarrollado una técnica que permite crecer a este tipo de microorganismos de manera mucho más sencilla de lo que hasta ahora se ha hecho. Creo que nos esperan grandes sorpresas de esta nueva saga con nombre vikingo.